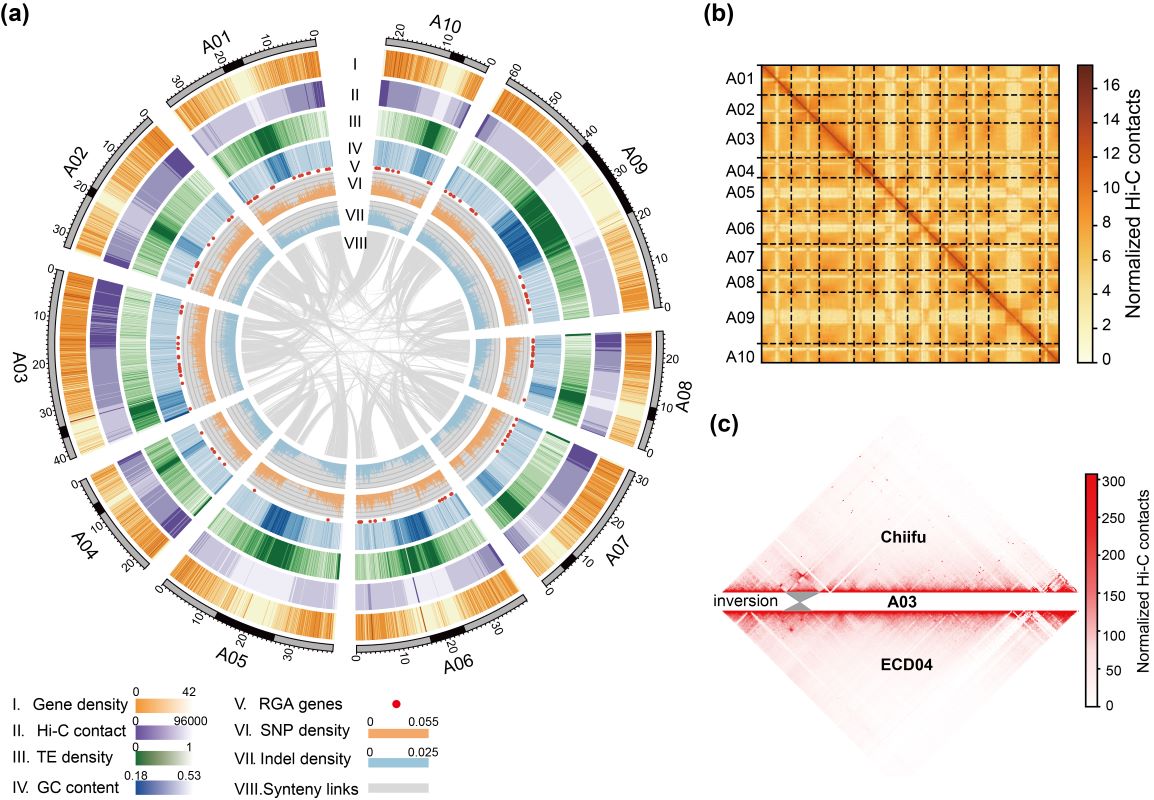
图1 欧洲芜菁ECD04的基因组和Hi-C交互图谱

图2 CRA8.2.4位点抗根肿病的功能验证
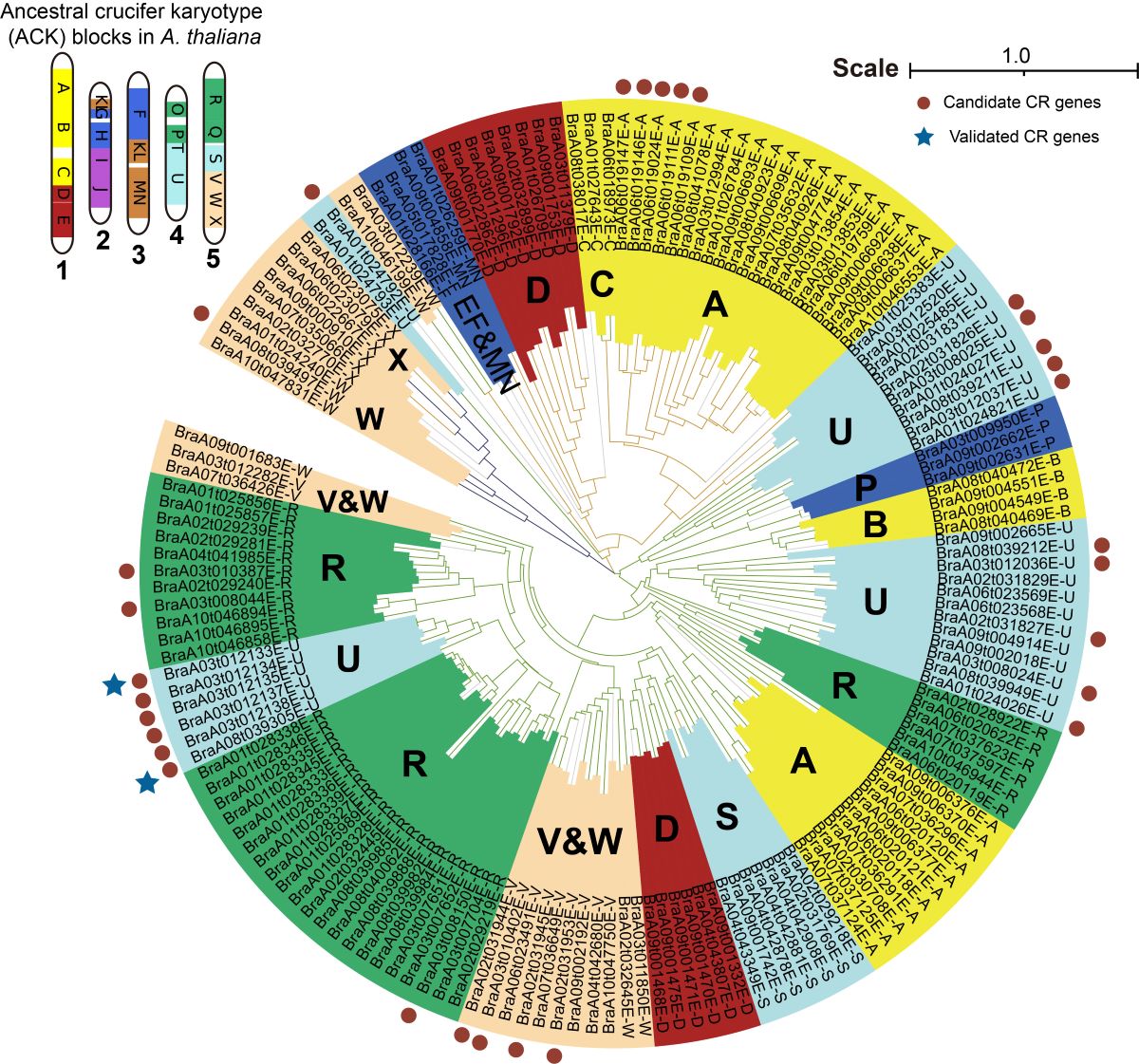
图3 根肿病抗性基因的系统发育树
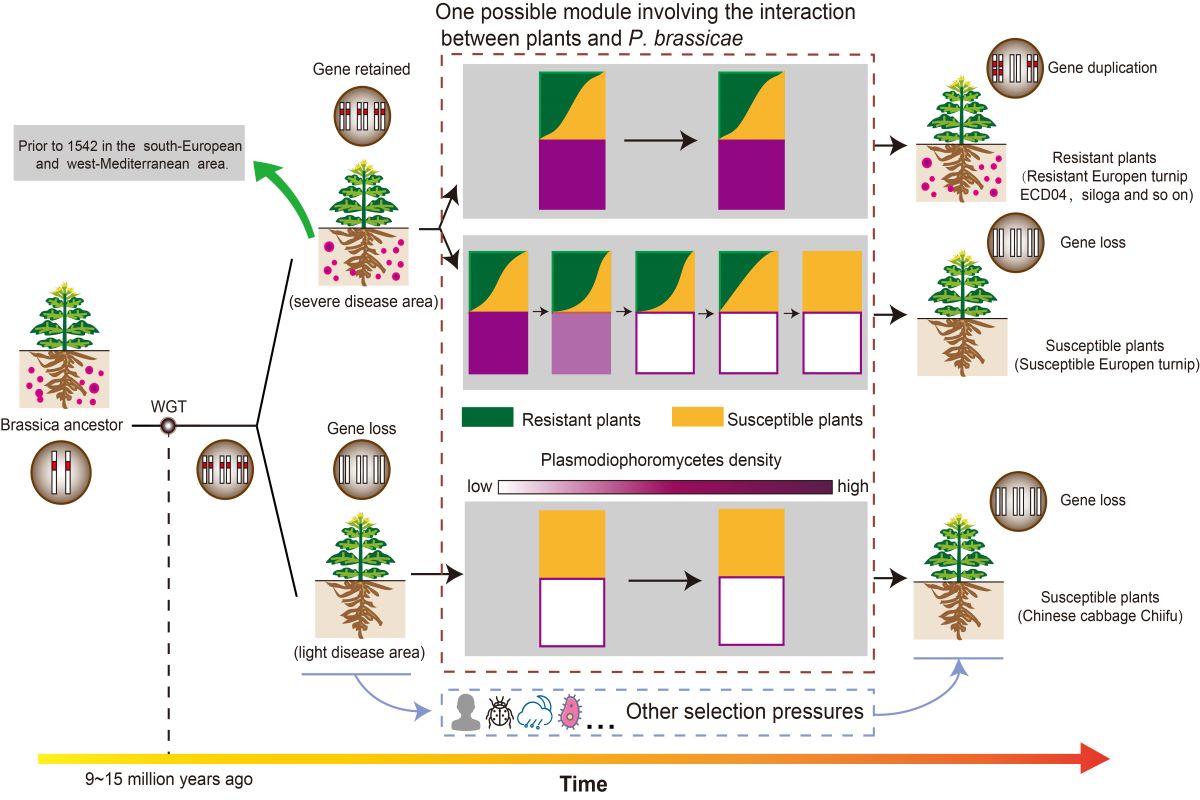
图4 芸苔属植物进化过程中根肿菌抗性基因的演化模型
南湖新闻网讯(通讯员 杨植全 江莹芬)近日,公司油菜团队张椿雨教授、杨庆勇教授课题组与沈阳农业大学朴钟云教授团队合作研究成果以“R gene triplication confers European fodder turnip with improved clubroot resistance”为题在Plant Biotechnology Journal发表。研究利用抗根肿病的欧洲芜菁ECD04参考基因组,解析芸薹属根肿病抗性基因的演化历程,为十字花科作物抗根肿病基因的克隆、标记开发,以及抗性育种提供了重要参考。
根肿病(Clubroot),被称作“十字花科癌症”,是一种由根肿病菌(Plasmodiophora brasicae)引起的一种土传性病害,通常会导致作物根系形成大量的肿瘤,从而阻碍作物从土壤中吸收养分与水分,严重者整株作物枯死。十字花科包含许多重要的蔬菜、油料和饲料作物,在我国分布广、面积大,影响非常广泛,对稳定安全供给粮油、推进三产融合、助力乡村振兴等方面有重要作用。我国每年约320~400万公顷十字花科作物遭受根肿病的危害,发病严重的地区损失可达到60%以上甚至绝收,因此根肿病的防治已经成为一个重要的战略问题,从源头选育根肿病抗性品种被认为是控制根肿病蔓延最有效的策略之一。目前发现的根肿病抗性基因大多来自芸薹属A基因组,其中大部分的抗性位点来源于欧洲芜菁。但高质量的抗根肿病(Clubroot Resistance,CR)材料的参考基因组的缺乏严重阻碍了对A基因组中抗性基因的作用机制理解和育种实践中的挖掘与利用。
研究人员在研究中选用了具有多个抗性位点的ECD04抗根肿病欧洲芜菁,采用第三代PacBio测序技术结合染色体构象捕获(Hi-C)技术,成功组装了“ECD04”的基因组,获得了染色体水平的参考基因组序列(图1),并将已报道的28个抗根肿病位点进行了系统地整合,鉴定到62个抗根肿病候选基因,并通过转基因和接菌实验验证了两个位点中的候选基因CRA3.7.1和CRA8.2.4对根肿病抗性的功能(图2)。该研究通过比较基因组学和系统发育分析发现多个候选CR基因均来自祖先基因组的U区段(图3)。通过与盐芥基因组的共线性分析发现,CRA3.7.1和CRA8.2.4在芸薹属三倍化之前的祖先基因组中已经存在。比较基因组学分析结果进一步表明,感病的白菜和油菜基因组的CRA3.7.1和CRA8.2.4序列存在大片段的结构变异以及转座子插入,可能与其抗性的缺失有关。
基于以上结果,研究提出芸薹属作物根肿病抗性基因的进化演化模型(图4):全基因组三倍化使得祖先基因组中的抗性基因加倍,增强了植株对根肿病的抗性。在芸薹属植物与病菌长期互作和进化过程中,三种互作模式共同存在:1)宿主与病菌达到了动态平衡状态,抗根肿病基因受到强烈正选择而一直保留;2)宿主中根肿病抗性逐渐增加,限制了根肿病菌扩散直至逐渐消失,最终导致抗根肿病基因功能丧失;3)人类的活动使得芸薹属植株传播到其它没有根肿病的地区,导致抗性基因功能逐渐丧失。
太阳集团成博士杨植全(现广州大学博士后)和植物科学技术学院博士江莹芬(现安徽省农业科学院作物研究所副研究员)为论文共同第一作者。植物科学技术学院张椿雨教授、太阳集团成杨庆勇教授和沈阳农业大学园艺学院朴钟云教授为该论文通讯作者。作物遗传改良国家重点实验室周永明教授、李再云教授在该研究过程中提供了重要指导和帮助。本项目得到国家自然科学基金项目,国家现代农业产业技术体系和中央高校基本科研业务费专项资金等项目资助。
审核人:杨庆勇
【英文摘要】
Clubroot is one of the most important diseases for many important cruciferous vegetables and oilseed crops worldwide. Different clubroot resistance (CR) loci have been identified from only limited species in Brassica, making it difficult to compare and utilize these loci. European fodder turnip ECD04 is considered as one of the most valuable resources for CR breeding. To explore the genetic and evolutionary basis of CR in ECD04, we sequenced the genome of ECD04 using de novo assembly and identified 978 candidate R genes. Subsequently, the 28 published CR loci were physically mapped to 15 loci in the ECD04 genome, including 62 candidate CR genes. Among them, two CR genes, CRA3.7.1 and CRA8.2.4, were functionally validated. Phylogenetic analysis revealed that CRA3.7.1 and CRA8.2.4 originated from a common ancestor before the whole genome triplication (WGT) event. In clubroot susceptible Brassica species, CR-gene homologs were affected by transposable element (TE) insertion, resulting in the loss of CR function. It can be concluded that the current functional CR genes in Brassica rapa and non-functional CR genes in other Brassica species were derived from a common ancestral gene before WGT. Finally, a hypothesis for CR gene evolution is proposed for further discussion.
